Biomolekulêre struktuur
Biomolekulêre struktuur is die ingewikkelde gevoude, driedimensionele vorm wat gevorm word deur 'n molekuul proteïen, DNS (DNA) of RNS (RNA), en dit is belangrik vir die funksie daarvan. Die struktuur van hierdie molekules kan oorweeg word by enige van verskeie lengteskale wat wissel van die vlak van individuele atome tot die verhoudings tussen hele proteïen-subeenhede. Hierdie nuttige onderskeid tussen skale word dikwels uitgedruk as 'n ontbinding van molekulêre struktuur in vier vlakke: primêre, sekondêre, tersiêre en kwaternêre. Die steier vir hierdie meervoudige organisasie van die molekule ontstaan op die sekondêre vlak, waar die fundamentele strukturele elemente die verskillende waterstofbindings van die molekuul is. Dit lei tot verskeie herkenbare domeine van proteïenstruktuur en nukleïensuurstruktuur, insluitende sulke sekondêre struktuur eienskappe soos alfa helixes en beta lakens vir proteïene, en haarspelde, bultjies en interne lusse vir nukleïensure.
Die terme primêre, sekondêre, tersiêre en kwaternêre struktuur is deur Kaj Ulrik Linderstrøm-Lang in sy 1951 Lane Mediese Lesings by Stanford Universiteit ingestel.
Primêre struktuur[wysig | wysig bron]
Die primêre struktuur van 'n biopolymeer is die presiese spesifikasie van sy atoomsamestelling en die chemiese bindings wat daardie atome verbind (insluitende stereochemie). Vir 'n tipiese onvertakte, ongekruiste biopolimeer (soos 'n molekule van 'n tipiese intrasellulêre proteïen, of van DNS of RNS), is die primêre struktuur gelyk aan die volgorde van sy monomeersubeenhede, soos peptiede of nukleotiede
Primêre struktuur word soms verkeerd genoem primêre volgorde, maar daar is nie so 'n term nie, sowel as geen parallelle konsep van sekondêre of tersiêre volgorde nie. By konvensie word die primêre struktuur van 'n proteïen aangemeld vanaf die aminoterminaal (N) na die karboksieterminaal (C), terwyl die primêre struktuur van DNS of RNS molekule vanaf die 5'-einde tot die 3'-einde gerapporteer word.
Die primêre struktuur van 'n nukleïensuurmolekule verwys na die presiese volgorde van nukleotiede wat die hele molekuul uitmaak. Dikwels koördineer die primêre struktuur volgordemotiewe wat van funksionele belang is. Enkele voorbeelde van sulke motiewe is: die C / D- en H / ACA-bokse van snoRNSs, LSm-bindingswerf wat voorkom in spliceosomale RNSE soos U1, U2, U4, U5, U6, U12 en U3, die Shine-Dalgarno-volgorde, die Kozak-konsensusvolgorde en die RNS-polimerase III-terminator[1]
Sekondêre struktuur[wysig | wysig bron]
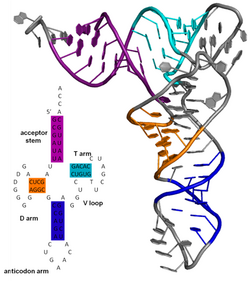
Die sekondêre struktuur is die patroon van waterstofbindings in 'n biopolimeer. Dit bepaal die algemene driedimensionele vorm van plaaslike segmente van die biopolimere, maar beskryf nie die globale struktuur van spesifieke atoomposisies in driedimensionele ruimte wat as tersiêre struktuur beskou word nie. Sekondêre struktuur word formeel gedefinieer deur die waterstofbindings van die biopolimeer, soos waargeneem in 'n atoomresolusiestruktuur. In proteïene word die sekondêre struktuur gedefinieer deur patrone van waterstofbindings tussen ruggraatamied en karboksielgroepe (kantketting-hoofketting en kantketting-kantketting waterstofbindings is irrelevant), waar die DSSP-definisie van 'n waterstofbinding gebruik word. In nukleïensure word die sekondêre struktuur gedefinieer deur die waterstofbinding tussen die stikstofbasisse.
Vir proteïene word die waterstofbinding egter met ander strukturele eienskappe gekorreleer, wat aanleiding gegee het tot minder formele definisies van sekondêre struktuur. Byvoorbeeld, in die algemeen, residu's in proteïen, herken helle ruggraat dihedrale hoeke in 'n deel van die Ramachandran plot; dus word 'n segment van residu en met sulke dihedrale hoeke dikwels 'n heliks genoem, ongeag of dit die korrekte waterstofbindings het. Baie ander minder formele definisies is voorgestel, wat dikwels konsepte uit die differensiële geometrie van krommes gebruik, soos kromming en torsie. Strukturele bioloë wat 'n nuwe atoomresolusiestruktuur oplos, sal soms sy sekondêre struktuur met die oog opdra en hul opdragte in die ooreenstemmende Proteïen Data Bank (VOB) lêer opteken.
Die sekondêre struktuur van 'n nukleïensuurmolekule verwys na die basisparingsinteraksies binne een molekuul of stel wisselende molekules. Die sekondêre struktuur van biologiese RNS'e kan dikwels uniek ontbind word in stingels en lusse. Dikwels kan hierdie elemente of kombinasies daarvan verder geklassifiseer word, bv. Tetraloops, pseudoknots en stamlusse. Daar is baie sekondêre struktuur elemente van funksionele belang vir biologiese RNS. Bekende voorbeelde sluit in die Rho-onafhanklike terminator stamlusse en die oordrag RNS (tRNS) klawerblad. Daar is 'n klein groep van navorsers wat probeer om die sekondêre struktuur van RNS molekules te bepaal. Benaderings sluit beide eksperimentele en berekeningsmetodes in (sien ook die lys van RNS struktuurvoorspellingsprogrammatuur).
Tersiêre struktuur[wysig | wysig bron]
Die tersiêre struktuur van 'n proteïen of enige ander makromolekule is sy driedimensionele struktuur, soos gedefinieer deur die atoomkoördinate. Proteïene en nukleïensure vou in komplekse driedimensionele strukture wat die molekules se funksies tot gevolg het. Alhoewel sulke strukture uiteenlopend en kompleks is, word hulle dikwels saamgestel uit herhalende, herkenbare tersiêre struktuurmotiewe en domeine wat as molekulêre boublokke dien. Tersiêre struktuur word beskou as grootliks bepaal deur die biomolekule se primêre struktuur (sy volgorde van aminosure of nukleotiede)
Kwaternêre struktuur[wysig | wysig bron]
Die kwaternêre struktuur verwys na die aantal en rangskikking van veelvoudige proteïenmolekules in 'n multi-subeenheidskompleks. Vir nukleïensure is die term minder algemeen, maar kan dit verwys na die hoër vlak organisasie van DNS in chromatien, insluitend die interaksies met histone, of die interaksies tussen afsonderlike RNA-eenhede in die ribosoom of spliceosoom.
Struktuurbepaling[wysig | wysig bron]
Struktuurondersoek is die proses waardeur biochemiese tegnieke gebruik word om biomolekulêre struktuur te bepaal. Hierdie analise kan gebruik word om die patrone te definieer wat gebruik kan word om die molekulêre struktuur, eksperimentele analise van molekulêre struktuur en funksie af te lei, en verdere begrip van die ontwikkeling van kleiner molekules vir verdere biologiese navorsing. Struktuurondersoekanalise kan gedoen word deur middel van baie verskillende metodes, wat chemiese probing, hidroksiel radikaalondersoek, nukleotied-analitiese interferensie kartering (NAIM) en in-lyn ondersoek insluit.
DNS-strukture kan bepaal word deur gebruik te maak van kernmagnetiese resonansspektroskopie of röntgenkristallografie. Die eerste gepubliseerde verslae (deur Rosalind Franklin en Raymond Gosling in 1953) van A-DNS-röntgendiffraksiepatrone – en ook B-DNS-ontledings gebaseer op Patterson-funksie-transformasies wat slegs 'n beperkte hoeveelheid strukturele inligting vir georiënteerde vesels van DNS geïsoleerd van kalf thymus. 'n Alternatiewe analise is dan deur Wilkins et al voorgestel. In 1953 vir B-DNS röntgendiffraksie en verstrooiingspatrone van gehidreerde, bakterie-georiënteerde DNA-vesels en forelspermkoppe in terme van vierkante Bessel-funksies. Alhoewel die '' B-DNS-vorm 'die algemeenste is onder die toestande wat in selle voorkom, is dit nie 'n goed gedefinieerde konformasie nie, maar 'n familie of fuzzy stel DNS-konformasies wat voorkom by die hoë hidrasie vlakke wat teenwoordig is in 'n wye verskeidenheid lewende organismes. selle. Hul ooreenstemmende X-straaldiffraksie- en verstrooiingspatrone is kenmerkend van molekulêre parakristalle met 'n beduidende mate van wanorde (meer as 20%), en die struktuur is nie tracteerbaar deur slegs die standaardanalise te gebruik nie.
In teenstelling hiermee word die standaardanalise, wat slegs Fourier-transformasies van Bessel-funksies en DNS molekulêre modelle behels, steeds roetine gebruik om A-DNS en Z-DNS-röntgendiffraksiepatrone te analiseer. [2]
Struktuurvoorspelling[wysig | wysig bron]

Biomolekulêre struktuurvoorspelling is die voorspelling van die driedimensionele struktuur van 'n proteïen vanuit sy aminosuurvolgorde, of van 'n nukleïensuur uit die nukleobase (basis) volgorde. Met ander woorde, dit is die voorspelling van sekondêre en tersiêre struktuur van sy primêre struktuur. Struktuurvoorspelling is die omgekeerde van biomolekulêre ontwerp, soos in rasionele ontwerp, proteïenontwerp, nukleïensuurontwerp en biomolekulêre ingenieurswese.
Proteinstruktuurvoorspelling is een van die belangrikste doelstellings wat deur bioinformatika en teoretiese chemie nagestreef word. Proteinstruktuurvoorspelling is van groot belang in medisyne (byvoorbeeld in geneesmiddelontwerp) en biotegnologie (byvoorbeeld in die ontwerp van nuwe ensieme). Elke twee jaar word die prestasie van huidige metodes geassesseer in die Kritieke Assessering van Proteïenstruktuurvoorspelling (KASP) eksperiment.
Daar is ook 'n beduidende hoeveelheid bioinformatika-navorsing gerig op die RNS-struktuurvoorspellingsprobleem. 'N Algemene probleem vir navorsers wat met RNS werk, is om die driedimensionele struktuur van die molekuul te bepaal wat slegs die nukleïensuurvolgorde gegee het. In die geval van RNS word egter baie van die finale struktuur bepaal deur die sekondêre struktuur of intra-molekulêre basis-paringsinteraksies van die molekuul. Dit word getoon deur die hoë bewaring van basisparings oor verskillende soorte
Sekondêre struktuur van klein nukleïensuurmolekules word grootliks bepaal deur sterk, plaaslike interaksies soos waterstofbindings en basisstapeling. Die opsomming van die vrye energie vir sulke interaksies, gewoonlik met behulp van 'n naaste buur-metode, bied 'n benadering vir die stabiliteit van die gegewe struktuur. Die maklikste manier om die laagste vrye energie struktuur te vind, is om alle moontlike strukture te genereer en die vrye energie vir hulle te bereken, maar die aantal moontlike strukture vir 'n ry verhoog eksponensieel met die lengte van die molekule. Vir langer molekules is die aantal moontlike sekondêre strukture groot.
Opeenvolgingskovariasiemetodes maak staat op die bestaan van 'n datastel wat saamgestel is uit veelvuldige homoloë RNS-reekse met verwante maar uiteenlopende rye. Hierdie metodes analiseer die kovariasie van individuele basisse in evolusie; Instandhouding by twee wyd geskeide terreine van 'n paar basiese paar nukleotiede dui op die teenwoordigheid van 'n struktureel benodigde waterstofbinding tussen daardie posisies. Die algemene probleem van pseudoknota-voorspelling is NP-voltooi.[3]
Ontwerp[wysig | wysig bron]
Biomolekulêre ontwerp kan beskou word as die omgekeerde van struktuurvoorspelling. In struktuurvoorspelling word die struktuur vanuit 'n bekende volgorde bepaal, terwyl in nukleïensuurontwerp 'n ry wat 'n gewenste struktuur sal vorm, gegenereer word.
Ander biomolekules[wysig | wysig bron]
Ander biomolekules, soos polisakkariede, polifenole en lipiede, kan ook 'n hoër-orde struktuur van biologiese gevolg hê.
Sien ook[wysig | wysig bron]
- Vergelyking van nukleïensuursimulasie sagteware
- Genestruktuur
- Lys van RNS struktuurvoorspelling sagteware
- Nie-koderende RNS
Verwysings[wysig | wysig bron]
- ↑ Bogenhagen, D. F.; Brown, D. D. (1981). "Nucleotide sequences in Xenopus 5S DNA required for transcription termination". Cell. 24 (1): 261–270. doi:10.1016/0092-8674(81)90522-5. PMID 6263489.
- ↑ http://planetphysics.org/encyclopedia/BesselFunctionsApplicationsToDiffractionByHelicalStructures.html.
- ↑ Lyngsø, R. B. (2000). "RNA pseudoknot prediction in energy-based models". J. Comput. Biol. 7 (3–4): 409–427. doi:10.1089/106652700750050862.
